生物学中的多模态融合
在单细胞和更广义的计算生物学中,“多模态”可以指很多类型的数据:DNA 序列、RNA 表达、染色质可及性、蛋白质水平、扰动响应、知识图谱、文本等。真正困难的地方通常不是列出有哪些模态,而是决定如何把它们融合起来。
这篇文章整理自最近一次报告的笔记。我尝试把相关方法概括为三类:自底向上、并行和统一。三类方法对“生物结构在哪里体现”以及“不同模态应该在模型的哪个位置相遇”给出了不同答案。
多模态任务
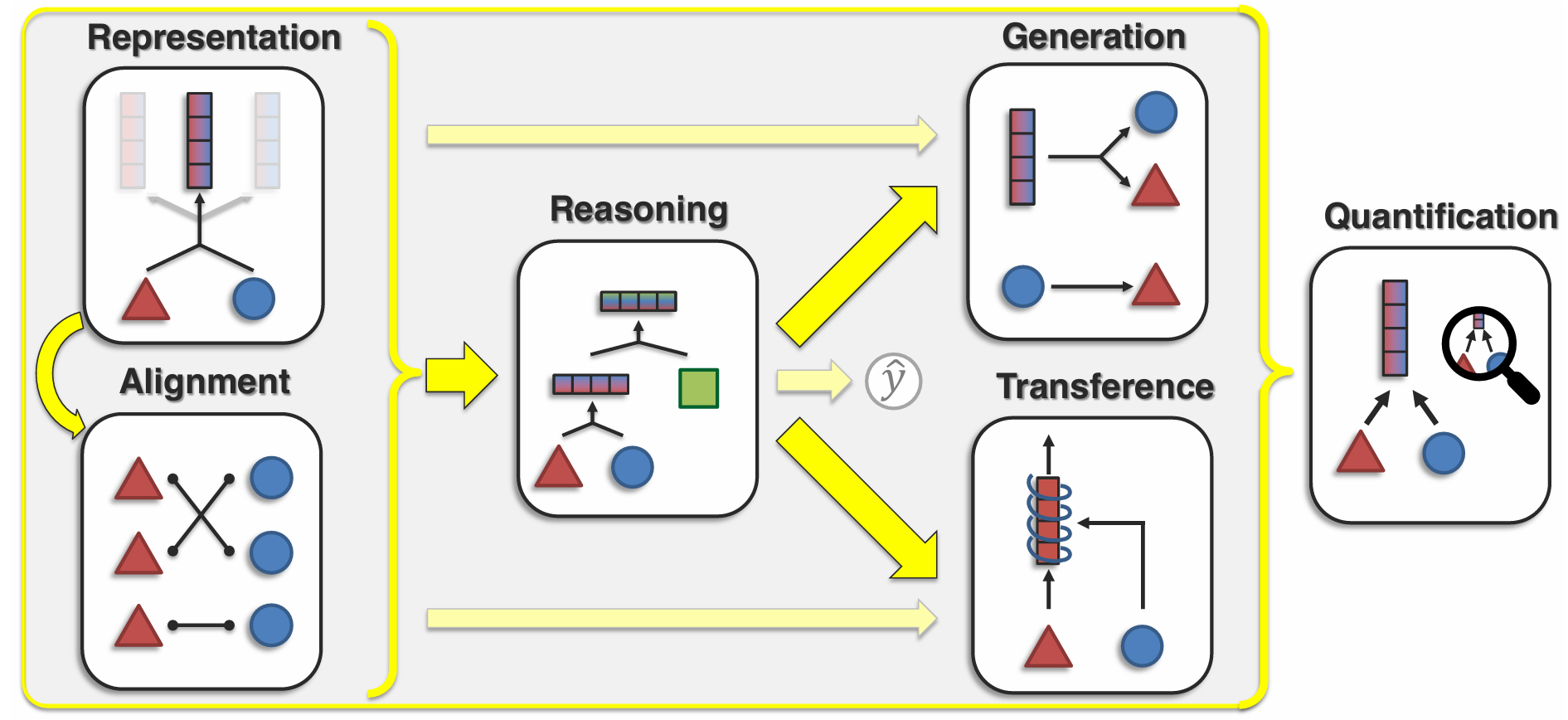
在确定模型架构之前,首先要明确我们希望多模态生物模型完成什么任务,例如跨模态预测、扰动响应预测、细胞状态推断、序列到功能预测等。不同任务会把模型架构推向不同方向。本文后面的讨论,只有放在具体预测目标的背景下才有意义。
自底向上方法
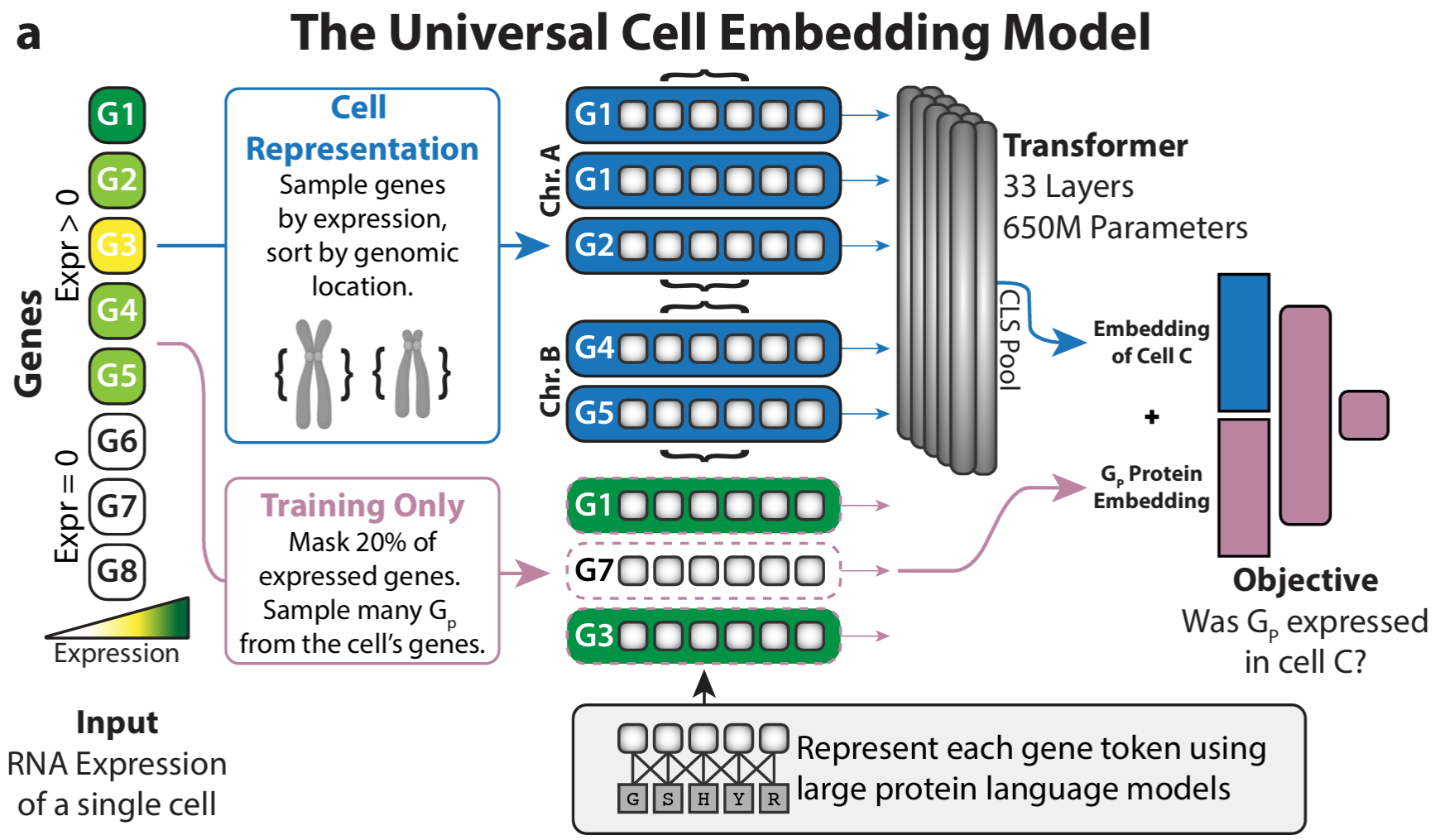
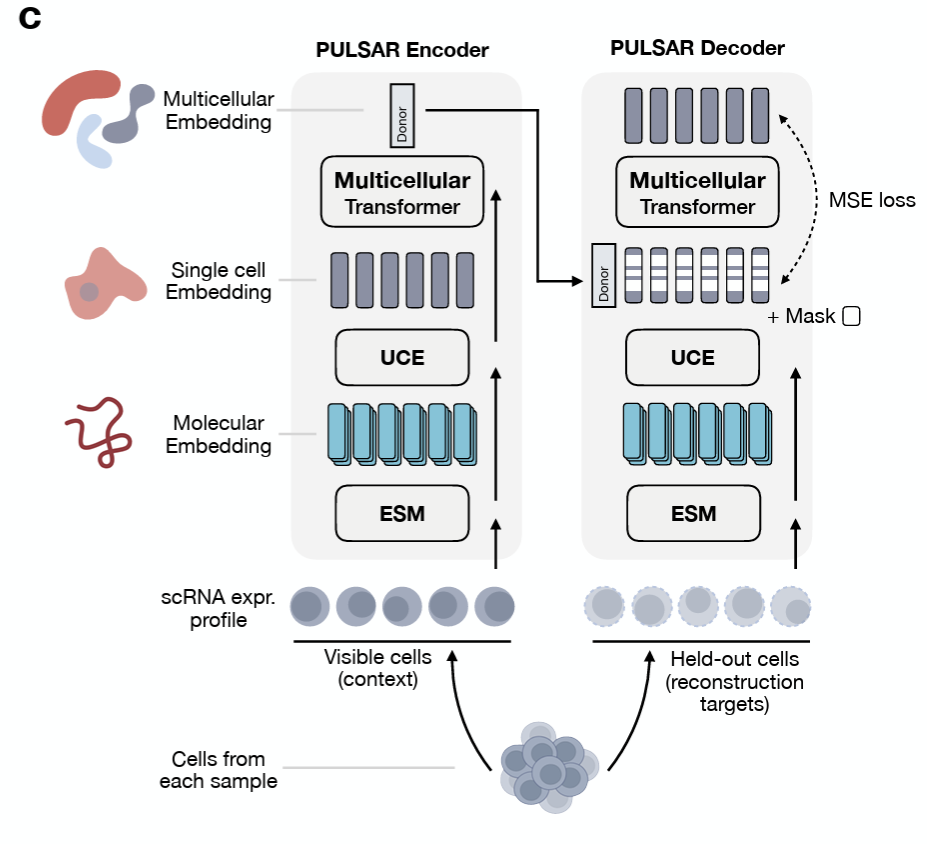
自底向上的方法沿着生物学的自然层级构建表示:分子 -> 细胞 -> 多细胞系统。类似 UCE 的模型从基因级 token 中学习细胞嵌入;PULSAR 等模型进一步走向组织和多细胞层面的结构。每一层都在该尺度上最丰富的数据上训练,下一层则继承来自下层的表示基础。
这种方法的优势是每个层级都有相对清晰的生物学解释,并且可以独立预训练。代价是,随着层级向上推进,误差和偏差也可能逐层累积。
从序列到扰动
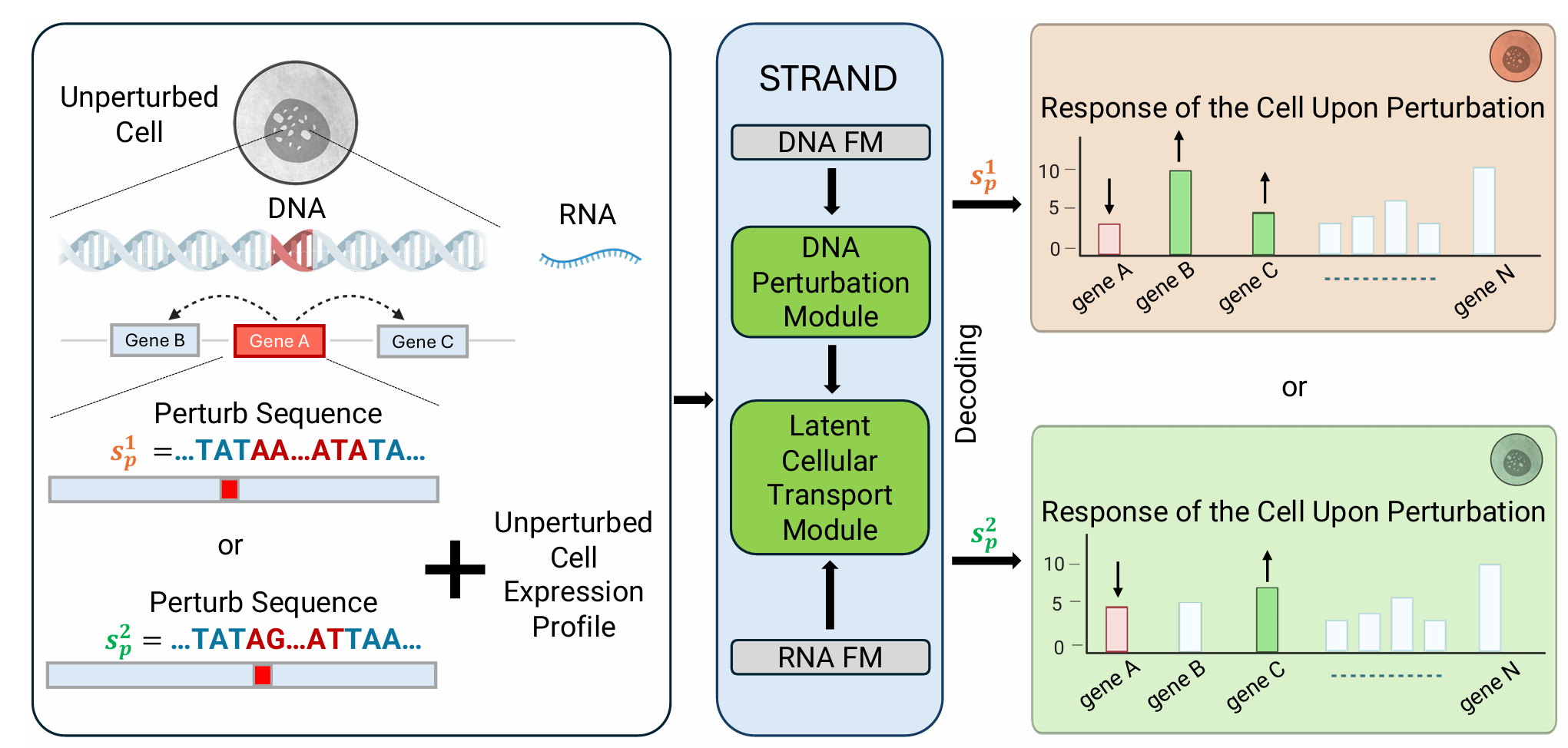
自底向上路线的一个具体例子是:从基因组序列出发,训练可以迁移到扰动预测任务的表示。这个链条可以概括为 序列 -> 表达 -> 响应。架构上的关键问题是:多模态信号应该在哪一个层级进入模型。
并行方法
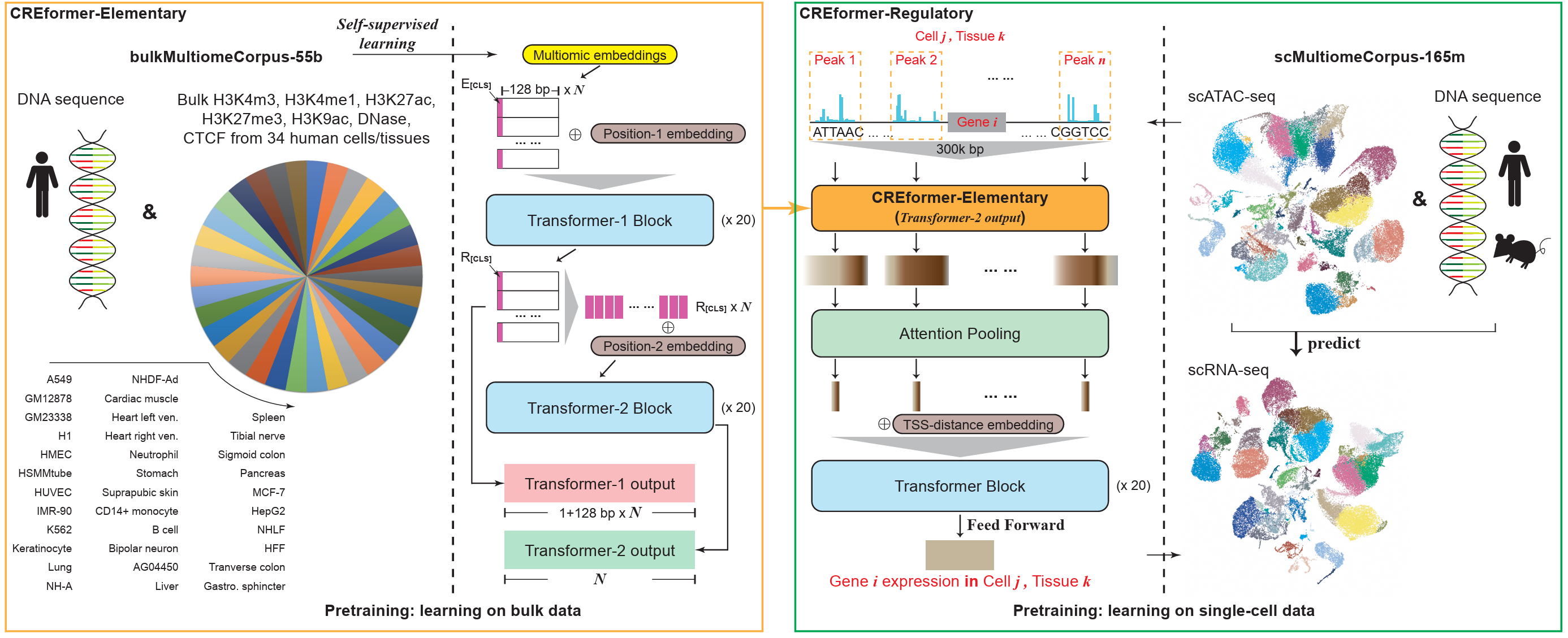
并行方法把不同模态视为大致平等的输入,并在输入阶段组合每个模态的嵌入。一个典型例子是:给定一段 DNA 序列和七条表观遗传轨迹,分别对每个模态做嵌入,然后直接把八个嵌入相加。后续模型看到的是一个已经融合好的向量。
这种方法成本低、容易按模态扩展,也很容易加入新的轨迹。问题在于,直接相加默认所有模态都处在同一个度量空间中,而这在生物学上往往并不成立。
每个模态使用独立编码器
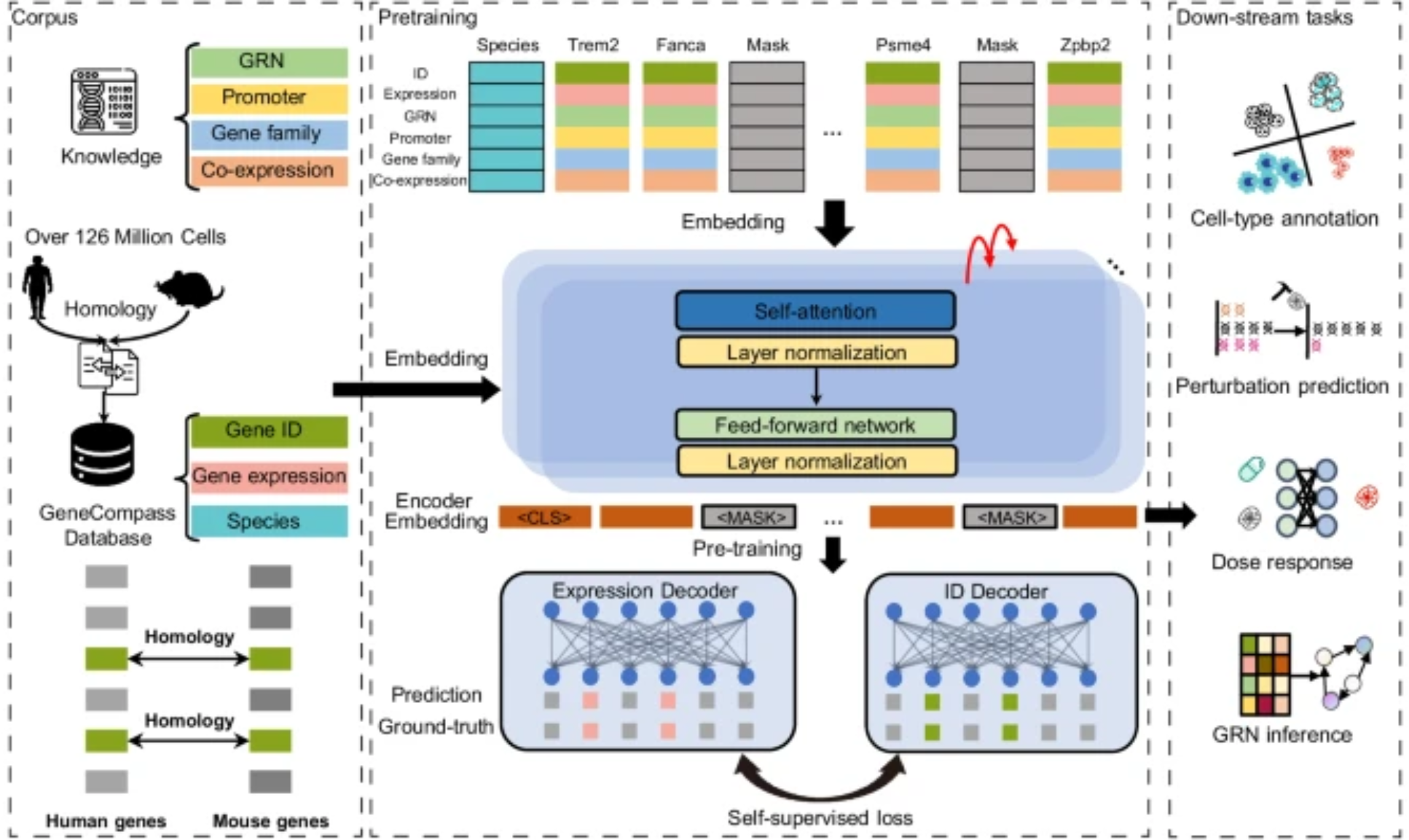
一种更谨慎的变体是:为每个模态保留独立编码器,并在更后面的阶段进行融合。每个编码器可以采用适合自身数据类型的 tokenization 和归纳偏置,融合则通过拼接、交叉注意力或门控机制完成,而不是在输入端直接相加。
不同知识来源
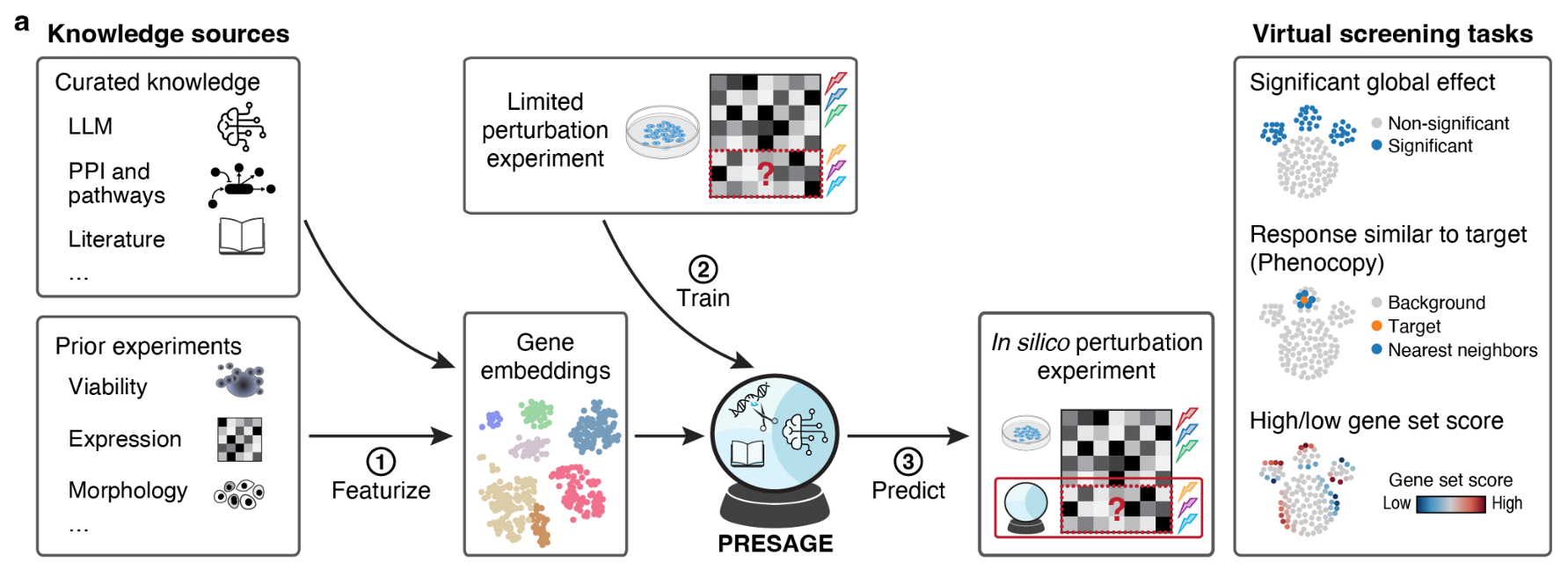
除了原始信号,多模态也可以表示不同类型的知识融合:用 LLM 提供文本上下文,用知识图谱提供人工整理的关系,用表格特征提供工程化先验。两种 pooling 策略反复出现:
- 全局 pooling:对不同来源的嵌入做加权平均。
- 基于注意力的 pooling:让 query 决定哪些来源更重要。
当每个来源的重要性会随样本变化时,后者通常更有效。
统一方法
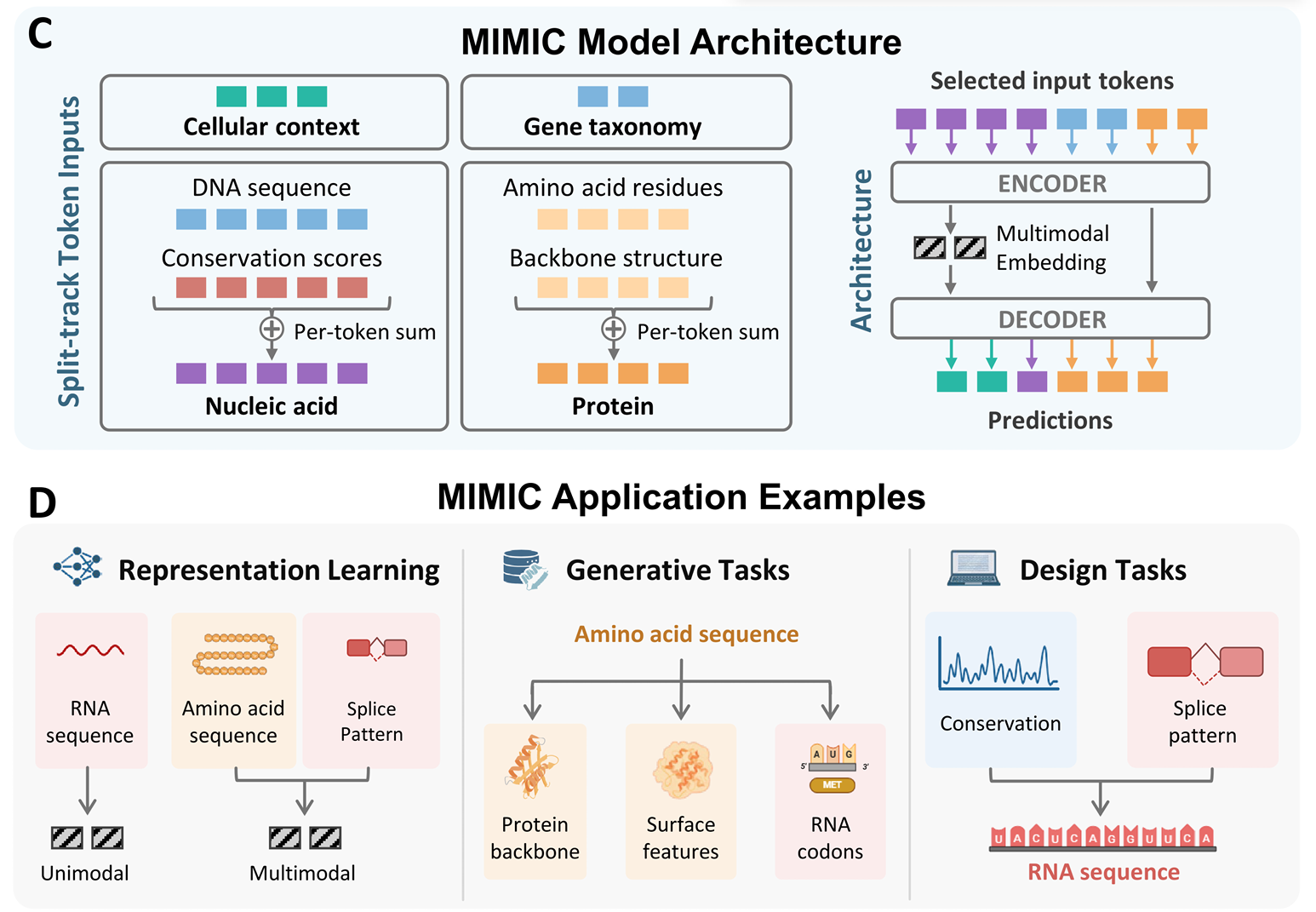
统一方法走的是与“每个模态一个编码器”相反的方向:把多个序列串联成一个统一的 token 流,然后交给同一个模型处理。与序列相关的任务,例如 DNA、RNA、蛋白质,天然适合这种形式,因为它们本来就共享 token 序列的形态。
这种简洁性很有吸引力:一个模型、一个损失函数、不需要额外的融合模块。困难在于,单个模型必须同时理解非常不同的统计规律,例如密码子使用偏好和调控 motif 的差异。
面向生物学的关系 Transformer
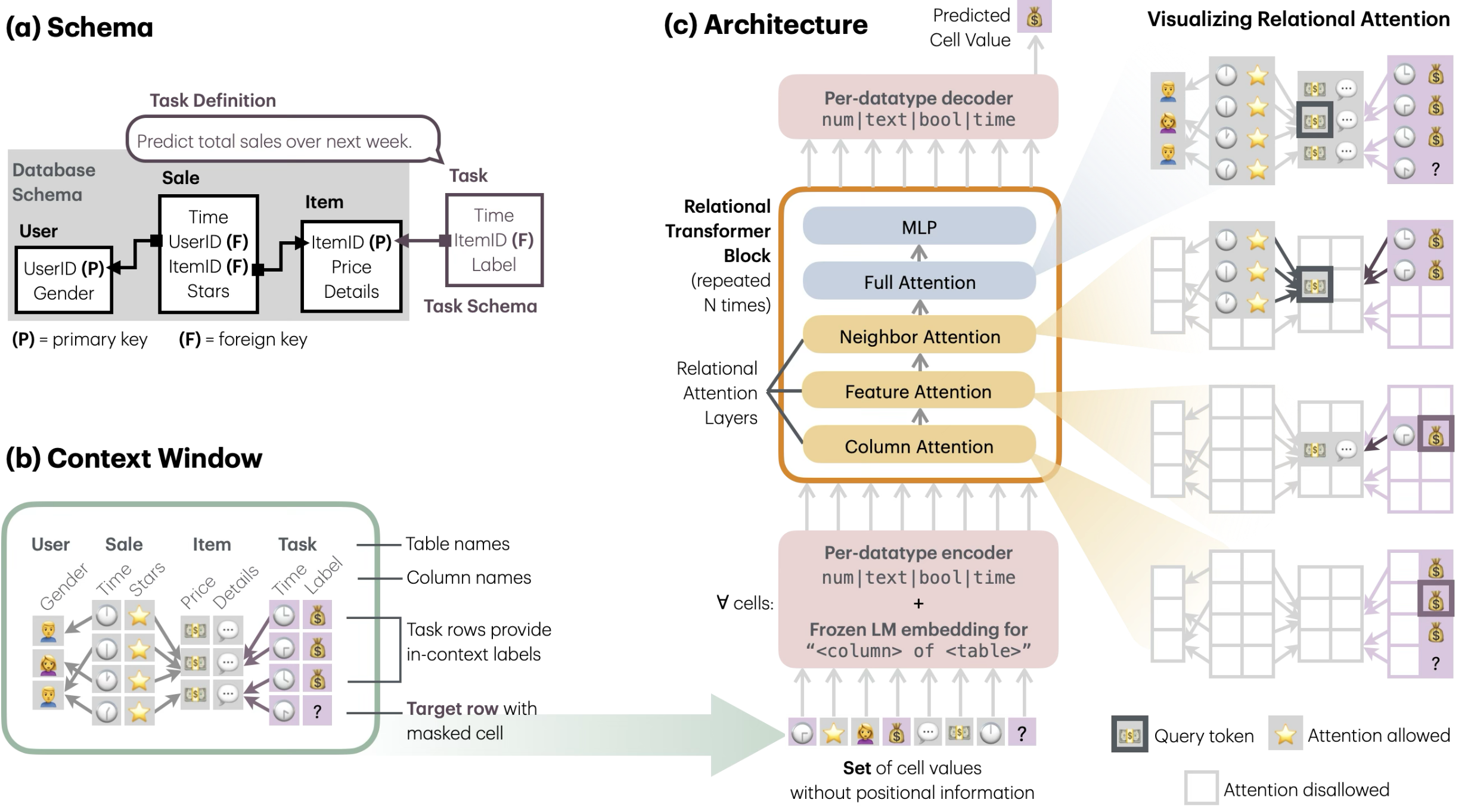
我目前最感兴趣的架构是关系 Transformer:不再把所有模态强行压进单一的融合瓶颈,而是把生物实体(基因、细胞、区域等)表示为节点,并让注意力在带类型的关系上进行计算。
细节
其中有两类注意力模式最关键:
- 关系注意力:用于互补模态,即每个模态都提供其他模态没有的信息。模型在每一层跨模态选择信息。
- 层级注意力:用于层级化模态,即结构本身是嵌套的,例如区域 -> 基因 -> 细胞 -> 组织。注意力受到该层级结构约束。
我反复遇到的两个开放问题是:
- 内存约束。 跨模态注意力随 token 数量呈二次增长,而生物学输入通常很长。
- 配对数据约束。 训练关系注意力需要多个模态同时被观测到的样本,而真正大规模配对的多模态数据仍然稀缺。
这些瓶颈是我认为下一阶段工作,无论是我自己的还是整个领域的,都需要重点解决的问题。
参考文献
- Liang, P. P., Zadeh, A., & Morency, L.-P. (2024). Foundations & Trends in Multimodal Machine Learning: Principles, Challenges, and Open Questions. ACM Computing Surveys, 56(10). https://doi.org/10.1145/3656580
- Rosen, Y., Roohani, Y., Agrawal, A., Samotorcan, L., Quake, S. R., & Leskovec, J. (2023). Universal Cell Embeddings: A Foundation Model for Cell Biology. BioRxiv. https://doi.org/10.1101/2023.11.28.568918
- Pang, K., Rosen, Y., Kedzierska, K., He, Z., Rajagopal, A., Gustafson, C. E., Huynh, G., & Leskovec, J. (2025). PULSAR: a Foundation Model for Multi-scale and Multicellular Biology. BioRxiv. https://doi.org/10.1101/2025.11.24.685470
- Fu, B., Dasoulas, G., Gabbita, S., Lin, X., Gao, S., Su, X., Ghosh, S., & Zitnik, M. (2026). STRAND: Sequence-Conditioned Transport for Single-Cell Perturbations. ArXiv Preprint ArXiv:2602.10156. https://arxiv.org/abs/2602.10156
- Yang, Z., Fan, X., Lan, M., Tang, X., Zheng, Z., Liu, B., You, Y., Tian, L., Church, G., Liu, X., & Gu, F. (2024). Multimodal foundation model predicts zero-shot functional perturbations and cell fate dynamics. BioRxiv. https://doi.org/10.1101/2024.12.19.629561
- Yang, X., Liu, G., Feng, G., Bu, D., Wang, P., & others. (2023). GeneCompass: Deciphering Universal Gene Regulatory Mechanisms with Knowledge-Informed Cross-Species Foundation Model. BioRxiv. https://doi.org/10.1101/2023.09.26.559542
- Littman, R., Levine, J., Maleki, S., Lee, Y., Ermakov, V., Qiu, L., Wu, A., Huang, K., Lopez, R., Scalia, G., Biancalani, T., Richmond, D., Regev, A., & Hütter, J.-C. (2025). Gene-embedding-based prediction and functional evaluation of perturbation expression responses with PRESAGE. BioRxiv. https://doi.org/10.1101/2025.06.03.657653
- Golkar, S., Kovalic, J., Espejo Morales, I., Sledzieski, S., Cho, K., Cranmer, M., Ho, S., & others. (2026). MIMIC: A Generative Multimodal Foundation Model for Biomolecules. ArXiv Preprint ArXiv:2604.24506. https://arxiv.org/abs/2604.24506
- Ranjan, R., Hudovernik, V., Znidar, M., Kanatsoulis, C., Upendra, R., Mohammadi, M., Meyer, J., Palczewski, T., Guestrin, C., & Leskovec, J. (2025). Relational Transformer: Toward Zero-Shot Foundation Models for Relational Data. ArXiv Preprint ArXiv:2510.06377. https://arxiv.org/abs/2510.06377
Enjoy Reading This Article?
Here are some more articles you might like to read next: